Mad for Science è un percorso didattico-laboratoriale di carattere chimico-biologico nato dall’idea di legare scuola e territorio. È stato realizzato grazie alla vittoria del concorso bandito dalla DIASORIN, società leader nel settore delle biotecnologie, che ha reso disponibili attrezzature di elevato livello professionale, e successivamente è stato sviluppato nell’ambito del progetto PON “Sentieri Animati”, portato avanti da una rete di scuole locali, di cui il nostro istituto è capo-fila, con l’obiettivo di potenziare l’educazione al patrimonio culturale, artistico e paesaggistico.
Elemento centrale del percorso di laboratorio è lo studio dei lieviti viticolo-enologici nel contesto di Nizza Monferrato, dove la produzione di vini e attività ad essa correlate definiscono l’occupazione economica prevalente.
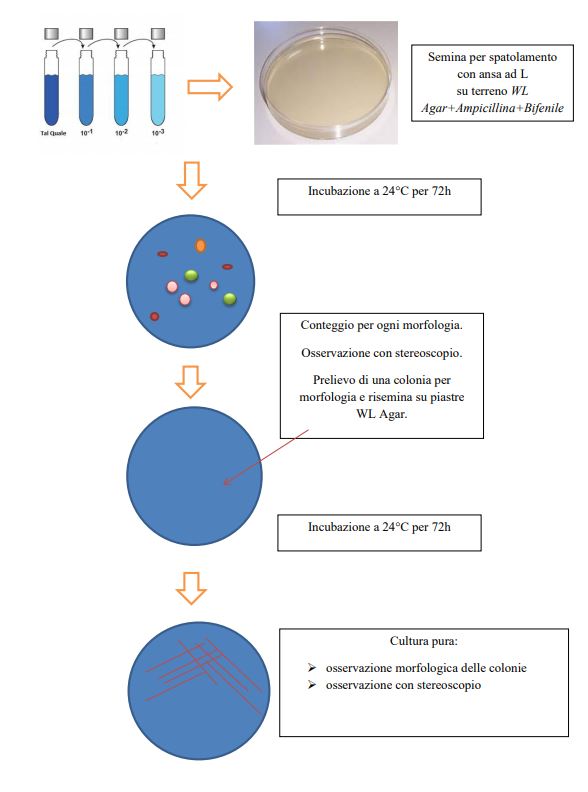
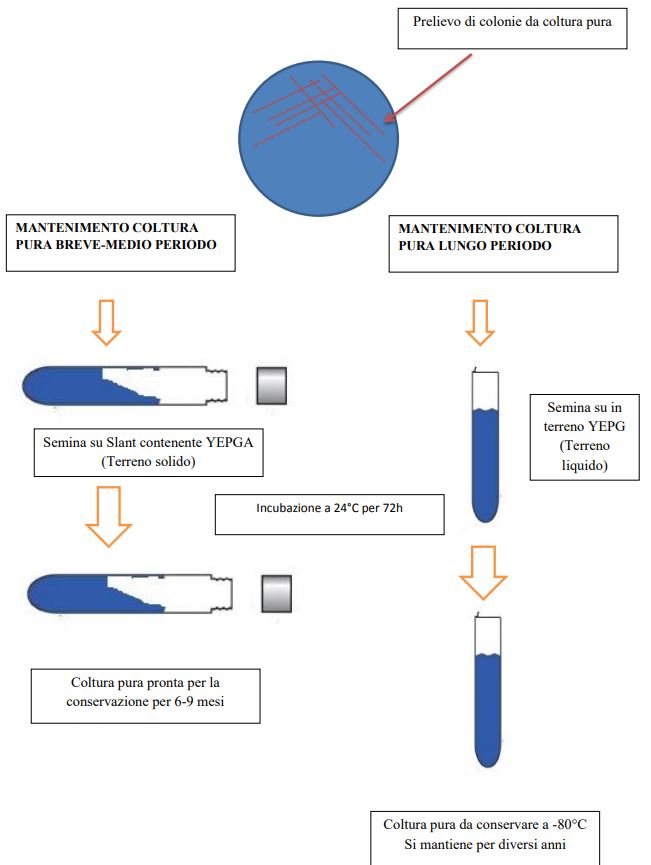
Lo studio di tali microrganismi è stato effettuato sia con tecniche classiche di Microbiologia, ossia coltivazione, isolamento ed identificazione, sia con tecniche di Biologia Molecolare basate sull’estrazione del DNA.
L’obiettivo del lavoro è monitorare la biodiversità dei lieviti coinvolti nella trasformazione dei mosti in pregiati vini partendo da campioni di uve prelevati da vigneti coltivati con metodi sia convenzionali sia biologici ottenuti grazie alla collaborazione di cantine locali.
Altro aspetto caratterizzante il progetto è la cooperazione con il centro di ricerca enologico CREA-ENO di Asti, che ha offerto consulenza nella raccolta dei dati archiviati in un database, ideato da alcuni ragazzi del Pellati, allo scopo di avere utili informazioni sui vigneti per analizzare le differenze nel tempo.
Dunque si tratta della scuola che si apre al mondo esterno con un progetto volto a conoscere e dare risalto alla biodiversità territoriale, operando scientificamente, alla stregua di un centro di ricerca, i cui risultati vengono restituiti alla comunità, provvedendo validi spunti per possibili applicazioni con l’obiettivo di tutelare e migliorare le risorse disponibili, riconoscendone il valore.




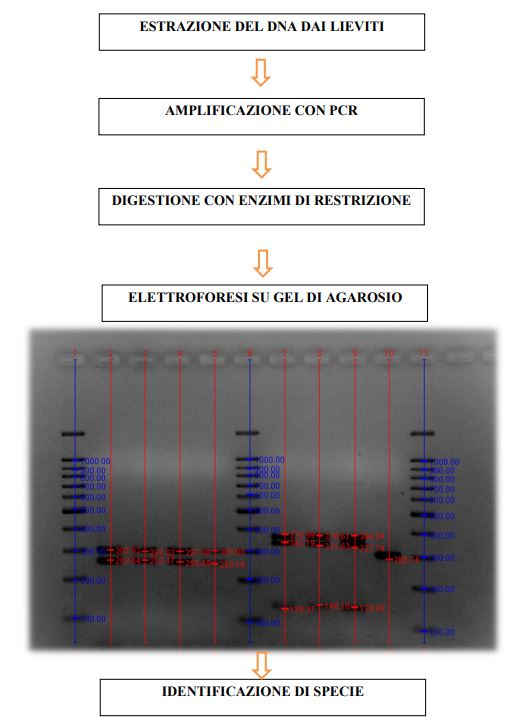

 A tal fine il laboratorio dispone di un software in grado di catturare un’immagine del profilo elettroforetico, facilitando l’interpretazione dei dati.
A tal fine il laboratorio dispone di un software in grado di catturare un’immagine del profilo elettroforetico, facilitando l’interpretazione dei dati.